次世代シーケンサー/Microarrayによるトランスクリプトーム解析に基づき、
がん・がんサブタイプ予測を可能にする解析プログラム・装置
Advantages
- トランスクリプトーム解析手法・装置・データセットの違いによる誤差に影響されない。
- 特定の腫瘍マーカーのみに限定するのではなく、網羅的データを活用する。
- がん以外の様々な疾患にも適用できる。
- 異なる網羅的解析スタディ間(マルチオミックス解析)にも適用できる。
Background and Technology
がん・がんサブタイプ診断を目的としたバイオマーカーの探索スタディが盛んであるが、がんは多様性をもつため、特定のバイオマーカーのみで診断することは難しい。したがって、網羅的な生体分子データの活用が重要だが、次世代シーケンサー/Microarrayによる網羅的解析では、解析の「場所・時期」「装置」など様々な要因で得られるデータに大きなずれが生じる(バッチ間誤差)。従来技術ではバッチ間誤差を補正できず、新規患者の検体データを既存の解析結果に当てはめてAIモデルを適用することが不可能だった。このような誤差に対しは、いくつかの遺伝子ペアの発現の大小関係のみを抽出し誤差を吸収する方法(k-TSP)等の報告があるが、これらの手法は情報量の大幅な削減によって誤差を吸収するよう設計されており、予測精度を犠牲にした手法である。
本発明は、次世代シーケンサー/microarrayの網羅的データを最大限に活用し、異なる手法・装置・データセットによる解析結果の比較・マージを可能にする解析方法および機械学習モデルである。本発明により、新規患者検体の次世代シーケンサー/microarrayデータによるがん・がんサブタイプの予測が可能になる。また、本発明はマルチオミクス解析による診断予測にも適用可能である。
Expectations
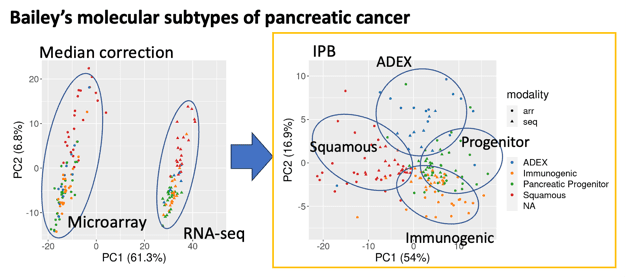
- 次世代シーケンサーとMicroarrayはモダリティの違いから得られるデータに大きな誤差が生じるが、本発明手法でこれらをマージし、Bailey et al.による膵がんのサブタイプ分類が可能であることを示した(図)。
- プログラム開発・専用装置開発・コスト検証を進めるため、トランスクリプトーム解析企業・次世代シーケンサー/Microarray装置メーカー・診断薬企業・臨床検査企業・解析プログラム企業等の協働パートナーを募集中。
- miRNA解析による早期がん診断や、個別化医療のためのサブタイプ診断への適用を目指している。
Publication
- AACR Special Conference in Cancer Research: Pancreatic Cancer (2023, Boston)
Researcher
馬場 泰輔 先生(名古屋大学医学部附属病院)
以下のフォームからお問い合わせください